研究課題
リグニン分解酵素発現を支配するカルモデュリン経路の解析
研究組織
| 代表者 | 入江俊一 (滋賀県立大学環境科学部) |
|---|---|
| 共同研究者 | 本田与一 (京都大学生存圏研究所) |
| 関連ミッション |
|
研究概要
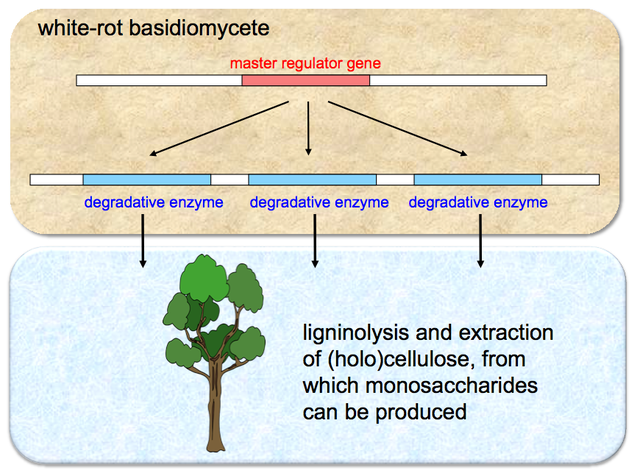
効率的な太陽エネルギー利用のためには、地球上最大のバイオマス量を占める木質資源の積極的利用が必要である。それにより、わが国の植林地保全にインセンティブを与える二次的効果も期待できる。これを実現するためには、木質資源を多様な形態の資源へ変換する必要があるが、ボトルネックとなるのは、セルロース・ヘミセルロースを被覆している難分解性物質、リグニンの除去である。リグニン除去については、物理・化学的方法よりも低コストで環境負荷が少ない生物的発酵法の開発が望まれている。白色腐朽菌と呼ばれる一群の担子菌は木質リグニンを完全に無機化する。しかし、分解開始の条件や分解経路の詳細については未解明の点が多く、そのことが産業的なバイオリアクターの開発を妨げている。これを解決するためには、従来のように個々の酵素遺伝子等を取り出して個別に解析するのではなく、木質リグニン分解に関する白色腐朽菌の環境応答の全貌を明らかとする必要がある。その情報により、リグニン分解機構全体を制御するマスターレギュレーター(Fig. 1)を特定し、それをターゲットにした分子育種や菌利用条件の改良も可能となる。
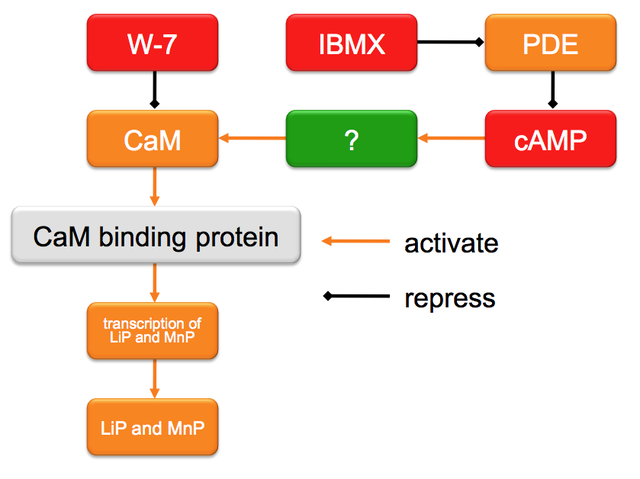
白色腐朽菌が分泌するリグニン分解酵素、特にリグニンペルオキシダーゼ(LiP)とマンガンペルオキシダーゼ(MnP)はリグニン分解の初発反応を担う重要な酵素とされている。これまでに、我々はモデル白色腐朽菌である Phanerochaete chrysosporium のトランスクリプトーム解析、阻害剤を用いた実験などから、Ca2+ シグナルの二次メッセンジャーであるカルモデュリン(CaM)が、lip および mnp 全アイソザイム遺伝子の発現を調節していることを明らかとした(Fig. 2)。CaM は様々な生理現象を調節していることで知られているが、LiP および MnP 発現についても重要な役割を果たすことが示されたことになる。次に、より詳細にリグニン分解酵素生産に関与する調節経路を特定するため、CaM相互作用タンパクの検索を行った。具体的には、ファージディスプレイ法にて P. chrysosporium 由来の CaM と結合するタンパク質を検索したところ、転写因子様タンパク質、低分子量 GTPase などの CaM 相互作用タンパク質の候補が数十個ほど検出された(Table 1)。
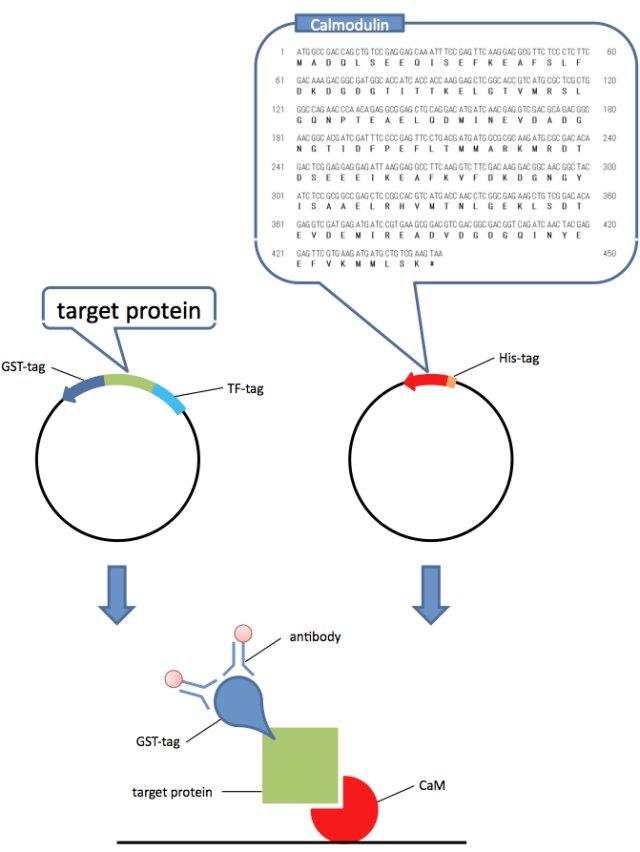
本研究は、推定的 CaM 相互作用タンパク質をコードする遺伝子をクローン化し、GST タンパク質との融合タンパク質として大腸菌で発現させる。それぞれの組換え大腸菌のライセートと His タグ付きの P. chrysosporium CaM タンパク質を混合し、His タグ結合性担体を用いたプルダウンを行う。得られたタンパク質について SDS-PAGE での電気泳動、抗 GST 抗体でのウエスタン分析を行い、目的タンパク質と CaM との結合性を慎重に判断する(Fig. 3)。CaM とCa2+ 依存的に相互作用することが確認されたタンパク質について、P. chrysosporium を宿主とした過剰発現、または発現抑制を行い、LiP および MnP 活性が受ける影響を観察する。酵素活性に変化が現れた組換え株については、lip および mnp 全アイソザイム遺伝子や他のリグニン分解関連遺伝子の転写物量測定、木質腐朽能力の測定などを行う。必要があれば、組換え株を対象としたトランスクリプトーム解析等も計画したい。 P. chrysosporium は検疫上の問題から国内での産業的利用には規制がある。育種ターゲットとして有用な遺伝子が特定された場合、国内自生の白色腐朽菌であるヒラタケについても、同様の遺伝子が働いているのかどうかを調査し、ヒラタケを中心とした育種を行う予定である。
Table 1 推定的 CaM 相互作用タンパク(一部)
| count | GO Desc | NCBI blastp |
| 37 | Xylose Reductase, A Dimeric Aldo-Keto Reductase From Candida Tenuis | |
| 8 | steroid metabolism | Yeast Oxysterol Binding Protein Osh4 In Complex With 7-Hydroxycholesterol |
| 4 | hydrolase activity | Putative Dienelactone Hydrolase From Klebsiella Pneumoniae Subsp. Pneumoniae Mgh 78578 |
| 3 | alcohol dehydrogenase activity, zinc-dependent | Arabidopsis Thaliana Double Bond Reductase (At5g16970)-Apo Form |
| 3 | adenosylhomocysteinase activity | Rat Liver S-Adenosylhomocystein Hydrolase |
| 2 | function unknown | |
| 2 | DNA binding | Yeast Nucleosome Core Particle Reveals Fundamental Differences In Inter-Nucleosome Interactions |
| 2 | small GTPase mediated signal transduction | Ras Related Protein Rras2 (Rras2) In The Gdp Bound State |
| 2 | carboxypeptidase A activity | |
| 2 | N-acetyltransferase activity | Structural Comparison Between Aspergillus Fumigatus And Human Gna1 |
| 2 | Marasmius Oreades Mushroom Lectin (Moa) In Complex With Galalpha(1,3)[fucalpha(1,2)]gal And Calcium | |
| 2 | peroxidase activity | Bacillus Stearothermophilus Glycerol Dehydrogenase |
| 2 | hydrolase activity, acting on carbon-nitrogen (but not peptide) bonds, in linear amides | Gamma Lactamase From Delftia Acidovorans |
| 2 | Eukaryotic Small Heat Shock Protein | |
| 1 | transcription factor activity | |
| 1 | calcium ion binding | Eps15-Eh2 Stonin2 Complex |
| 1 | The Ph Domain Of Pleckstrin Homology Domain-Containing Protein Family A Member 5 From Human |
ページ先頭へもどる
2011年8月2日作成